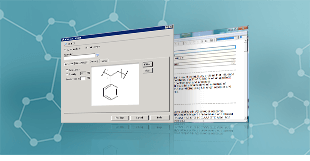
分子モデリング・
シミュレーションソフトウェア
Discovery Studio
Discovery Studio 2021
Discovery Studio最新のリリースでは、MSLD (Multi-Site Lambda Dynamics) のワークフローがより使いやすくなり、より多くの GPU 対応プラットフォームを導入することで研究を加速させます。
MSLD1 の作業がより快適に
- 既存の 3つのプロトコルを1つのプロトコル(MSLD Bias Optimization and Production)に統合し、GPU 対応プラットフォームでシンプルかつ高度な CHARMm シミュレーションを実現。
- 1 回のシミュレーションでコンビナトリアル・ライブラリ全体の相対結合自由エネルギーを計算し、競合的結合アッセイを模倣。
- 大規模バリデーションにより、初期のリード最適化段階で大規模な同族化合物ライブラリを探索する本研究手法の精度を確認。
- 自由エネルギー摂動法(FEP) よりも効率性が最大20倍向上。
CHARMm-DOMDEC による FEP 計算に対応
- 新しいプロトコル、CHARMm Relative FEP Calculations により、GPU 対応プラットフォーム(Linux) 上で両システム (リガンド系および複合体) の同時 FEP 計算が可能。
- 自由エネルギーを前進(Forward) と後退(Reverse) で予測。
- 終状態近傍でラムダの幅を狭めるカスタム・スケジュールを作成し、精度を向上させることが可能に。
原子タイプや力場のパラメータを追加
- CGenFF を利用して低分子の原子タイプを階層的に指定する、精度と一貫性に優れたスキームを利用可能。
- 力場の結合パラメータや角度パラメータを拡張・改善し、CGenFF力場を利用できるケミカルスペースを大幅に拡大。
生物製剤の粘度や凝集の予測に関する機能を強化
- Calculate Protein Formulation Properties プロトコルで Charge Map3 表面や Aggregation Scores3 表面を自動生成
タンパク質モデリング機能を強化
- RCSB Structure Search: 従来の検索 API が 2020 年 11 月に廃止されたのを受けて、新しい JSON クエリをサポートするように書き換えられました。
- BLAST Search (NCBI Server): パフォーマンスと信頼性が向上しました。
- Analyze Protein-Ligand Complexes: 入力に複数のタンパク質を指定できるようになりました。
- Predict Humanizing Mutations: パフォーマンスが向上し、生殖細胞系列ファイルの読み込みが容易になりました。
- Retrieve Antibody Templates from Database: 指定した抗体テンプレートをデータベースから取り込む際に利用できるサンプル・プロトコルが追加されました。
- BLAST PDB データベースと Swiss-Prot データベースが自動的にインストールされます。
ファーマコフォア・モデリング機能を強化
- リガンドベースのファーマコフォア・プロトコル、および Edit and Cluster Features ツールパネルで、非結合相互作用ファーマコフォア・フィーチャーがサポートされました。
- PharmaDB scPDB4 受容体- リガンド標的を更新し、非結合相互作用ファーマコフォア・フィーチャーが盛り込まれました。
- デフォルトのインストールで PharmaDB データベース全体が取り込まれ、必要なディスクスペースも 最大 10GB から 0.27GB に縮小されました。
GPU 対応プロトコルにより計算を高速化
- Dock Proteins (ZDOCK) プロトコル: CPU よりも最大 13 倍高速。
- Dynamics (NAMD) and Solvate with Explicit Membrane プロトコル: 1つの GPU で 8コア CPU よりも 7倍から 10倍高速。
- MSLD Bias Optimization and Production プロトコル: グリッド・サーバーと非グリッド・サーバーの両方で動作。
- CHARMm Relative FEP Calculations (GPU): 新たに DOMDECGPUによる FEP 計算をサポート。
お気軽にお問い合わせください
 電話でお問い合わせ
電話でお問い合わせ
- 東京(担当:SATグループ)
- 03-3520-3082
受付時間 9:00-17:30(土・日・祝除く)

 製造業向けITソリューション
製造業向けITソリューション  建設業務改善ソリューション
建設業務改善ソリューション  ビル管理業務支援 DK-CONNECT BM
ビル管理業務支援 DK-CONNECT BM FILDER CeeD TOP
FILDER CeeD TOP  FILDER CeeD 電気 TOP
FILDER CeeD 電気 TOP  Rebro D TOP
Rebro D TOP  データ・サイエンス・ソリューション Pipeline Pilot
データ・サイエンス・ソリューション Pipeline Pilot 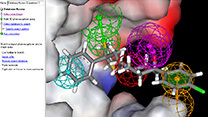 ライフサイエンス向けソフト Discovery Studio
ライフサイエンス向けソフト Discovery Studio 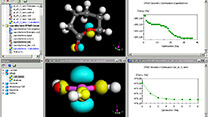 マテリアルサイエンス向けソフト Materials Studio
マテリアルサイエンス向けソフト Materials Studio 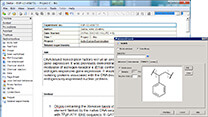 電子実験ノート
電子実験ノート 総合3DCG 制作ソフト Maya
総合3DCG 制作ソフト Maya  総合3DCG 制作ソフト 3ds Max
総合3DCG 制作ソフト 3ds Max  総合3DCG 制作ソフト MODO
総合3DCG 制作ソフト MODO  アニメーション制作ソフト Toon Boom
アニメーション制作ソフト Toon Boom